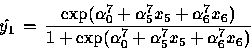
Avec l'option entropy, on obtient comme valeurs prédites les valeurs suivantes :
> res22b_nnet(bin9,y1,size=2,decay=0,entropy=T,maxit=200)
> cbind(y1,predict(res22b,bin9),y1- predict(res22b,bin9))
y1 val.predites ecart
1 0.72 0.720344484 -3.444839e-04
2 0.00 0.004017418 -4.017418e-03
3 0.83 0.830370486 -3.704858e-04
4 0.00 0.003962993 -3.962993e-03
5 0.52 0.517451704 2.548296e-03
6 0.02 0.003988040 1.601196e-02
7 0.92 0.915684402 4.315598e-03
8 0.05 0.050039370 -3.936961e-05
9 0.69 0.699828506 -9.828506e-03
10 0.55 0.547633708 2.366292e-03
11 0.00 0.004001075 -4.001075e-03
12 0.73 0.726522088 3.477912e-03
13 0.18 0.179853752 1.462477e-04
14 0.20 0.200233743 -2.337426e-04
15 0.00 0.003985559 -3.985559e-03
16 0.96 0.961960196 -1.960196e-03
On voit que l'on obtient les bonnes valeurs de y1.
On peut retrouver ces valeurs prédites en appliquant la formule de reconstitution.
On a donc :
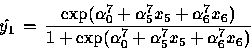
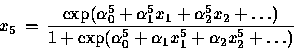
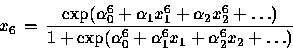
> summary(res22b) a 4-2-1 network with 13 weights options were - entropy fitting decay=0.00 0->5 1->5 2->5 3->5 4->5 0->6 1->6 2->6 3->6 4->6 0->7 5->7 6->7 -1.20 -3.9 3.04 -1.13 0.28 0.52 0.19 -0.54 1.26 -1.56 -1.55 -3.97 5.45 ss1_exp(-1.20-3.9*bin9[,1]+3.04*bin9[,2]-1.13*bin9[,3]+0.28*bin9[,4]) zz1_ss1/(1+ss1) ss2_exp(0.52+0.19*bin9[,1]-0.54*bin9[,2]+1.26*bin9[,3]-1.56*bin9[,4]) zz2_ss2/(1+ss2) ss_exp(-1.55-3.97*zz1+5.45*zz2) zz_ss/(1+ss) On obtient : > zz [1] 0.722576250 0.004056084 0.832753579 0.003997265 0.526203575 0.004025181 [7] 0.917054818 0.052828969 0.708985285 0.559964739 0.004038044 0.736632025 [13] 0.185221883 0.203269392 0.004021779 0.962311145Ce sont bien les valeurs prédites trouvées par la fonction ``predict''.