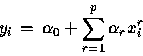
Analogie entre le perceptron multicouches sans couche cachée et la
régression linéaire
Le perceptron multicouches sans couche cachée peut être considérer comme une régression
linéaire (avec une fonction d'activation linéaire).
Nous allons donc, dans ce paragraphe, comparer la prédictivité d'un tel réseau
avec celle de la régression linéaire.
Dans ce cas, le passage des variables d'entrée à la variable de sortie est linéaire.
On a donc :
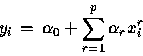
Remarquons que cette équation correspond bien à l'écriture du modèle de régression
où :
![]() y est la variable "réponse"
y est la variable "réponse"
![]()
![]() sont des variables réelles. On veut étudier leur
influence sur y.
sont des variables réelles. On veut étudier leur
influence sur y.
Comparaison de ces deux méthodes dans notre exemple
![]() Pour le réseau de neurones, on a ici :
Pour le réseau de neurones, on a ici :
![]() comme variables d'entrée la matrice "temp1[,1:3]"
comme variables d'entrée la matrice "temp1[,1:3]"
![]() comme variable de sortie yy
comme variable de sortie yy
![]() pas de variables dans la couche cachée. Donc "size=0"
pas de variables dans la couche cachée. Donc "size=0"
![]() une influence directe des variables d'entrée. Donc "skip=T"
une influence directe des variables d'entrée. Donc "skip=T"
![]() une fonction d'activation linéaire. Donc
"linout=T"
une fonction d'activation linéaire. Donc
"linout=T"
D'où la commande Splus suivante :
> rl1_nnet(temp1[,1:3],yy,size=0,decay=0,linout=T,skip=T,maxit=100)
On obtient ainsi les résultats suivants :
# weights: 4 initial value 1215.329472 iter 10 value 124.655154 final value 124.655146 convergedIci, 4 est le nombre de paramètres. L'algorithme converge vers la valeur 124.65 qui correspond à la valeur minimale de l'erreur quadratique.
Grâce à la commande "summary", on peut obtenir les poids des différentes connexions
qui correspondent en fait à l'estimation des paramètres
![]()
> summary(rl1) a 3-0-1 network with 4 weights options were - skip-layer connections linear output units 0->4 1->4 2->4 3->4 7.69 -0.05 1.12 -0.75On a ainsi :
![]() Pour la régression linéaire, on a les résultats suivants :
Pour la régression linéaire, on a les résultats suivants :
Call: lm(formula = V1 ~ X2 + X3 + X4, data = mat.rl)
Residuals:
Min 1Q Median 3Q Max
-4.158 -1.339 -0.5256 1.55 3.862
Coefficients:
Value Std. Error t value Pr(>|t|)
(Intercept) 7.6897 5.2681 1.4597 0.1592
X2 -0.0519 0.5481 -0.0946 0.9255
X3 1.1208 1.9693 0.5691 0.5753
X4 -0.7534 1.0825 -0.6960 0.4941
Residual standard error: 2.436 on 21 degrees of freedom
Multiple R-Squared: 0.05277
F-statistic: 0.39 on 3 and 21 degrees of freedom, the p-value is 0.7614
On remarque que nous avons les mêmes estimations des paramètres.
A l'aide de la commande "predict" et du résultat de la régression linéaire, on
calcule la somme des carrés de l'erreur à savoir :
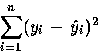
> critere_yy-predict(rl2,mat.rl) > critere_critere^2 > critere_sum(critere) [1] 124.6552On remarque aussi que nous retrouvons le critère à minimiser dans le réseau de neurones.
On a ainsi, par cet exemple, montré que le perceptron multicouches sans couche cachée était équivalent au modèle de régression linéaire.